表的内容
- 下一代测序(NGS)是一个强大的平台,可以对成千上万的人进行测序DNA同时分子。
- 下一代测序(NGS),也被称为高通量测序,是一个笼统的术语,用来描述许多不同的现代测序技术。
- 对低成本测序的高需求推动了高通量测序的发展,高通量测序一次产生数千或数百万个序列。
- 它们的目的是降低DNA测序的成本,超过标准染料终止剂方法所能达到的成本。
- 因此,这些最新的技术使我们能够比以前使用的桑格测序更快、更便宜地对DNA和RNA进行测序,并因此彻底改变了基因组学和分子生物学的研究。
NGS按不同世代分类,克服了传统DNA测序方法的局限性,在分子生物学的广泛应用中得到了应用。
它分为以下几代:
第一代
- 桑格测序
第二代测序
- 焦磷酸测序
- 可逆终止剂化学测序
- 通过结扎测序
第三代测序
- 单分子荧光测序
- 单分子实时测序
- 半导体测序
- 纳米孔测序
第四代测序
目的是直接在细胞中进行基因组分析。
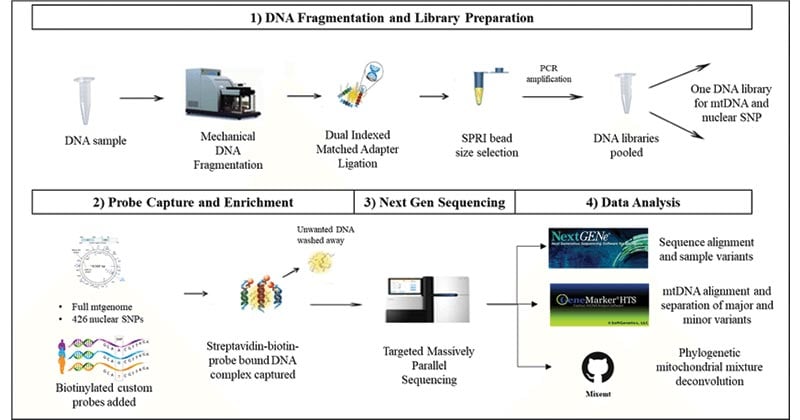
重要的下一代测序技术
Lynx therapeutics的大规模并行签名测序(MPSS)
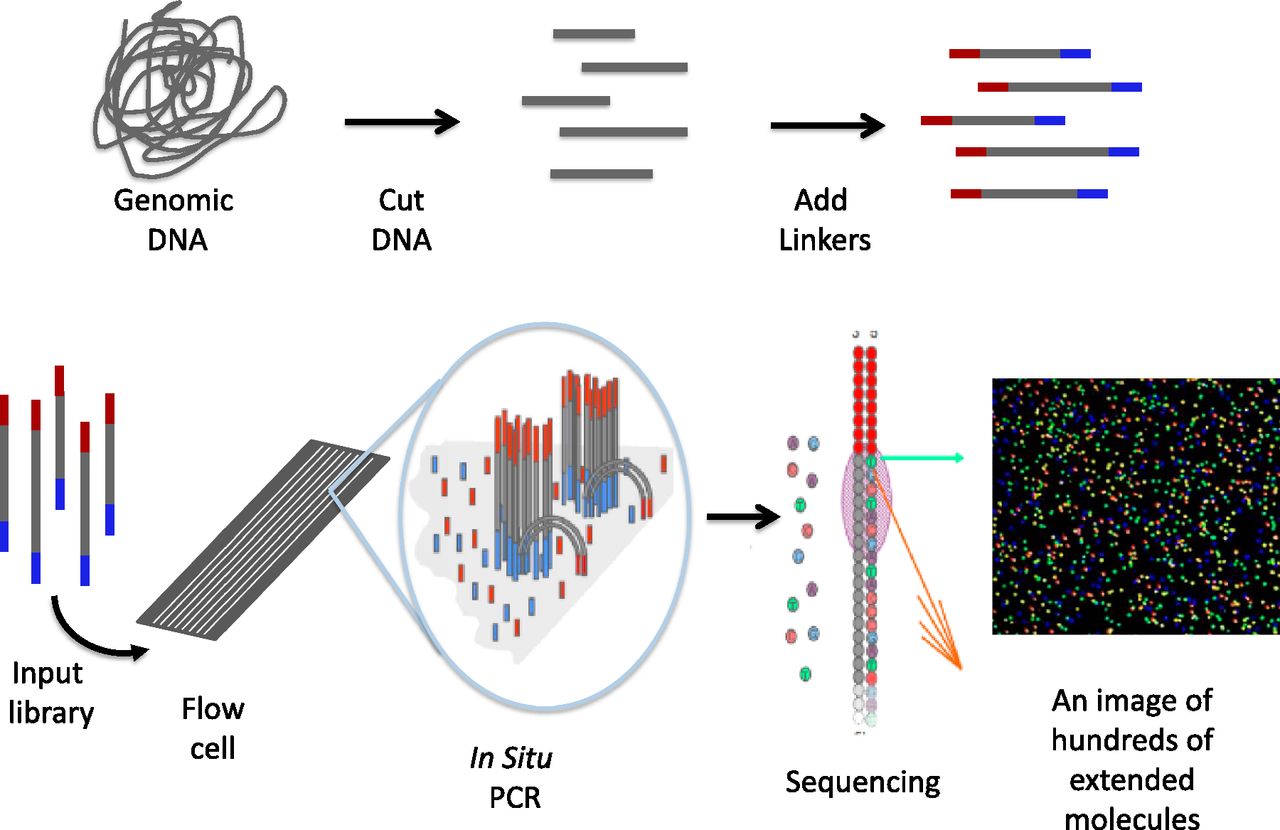
- 这被认为是第一个“下一代”测序技术。
- MPSS是在20世纪90年代由Lynx Therapeutics公司开发的,Lynx Therapeutics公司于1992年由Sydney Brenner和Sam eleter创建。
- MPSS是一种超高通量测序技术。
- 当应用于表达谱时,它可以揭示样本中几乎所有的转录本,并提供其准确的表达水平。
- MPSS是一种基于串珠的方法,它使用了一种复杂的方法:适配器连接,然后适配器解码,以四个核苷酸的增量读取序列;这种方法容易受到特定序列的偏差或特定序列的丢失。
- 然而,MPSS输出的基本属性是后来的“下一代”数据类型的典型特征,包括数十万个短DNA序列。
- 在MPSS的情况下,这些通常用于cDNA测序,以测量基因表达水平。
香肠测序
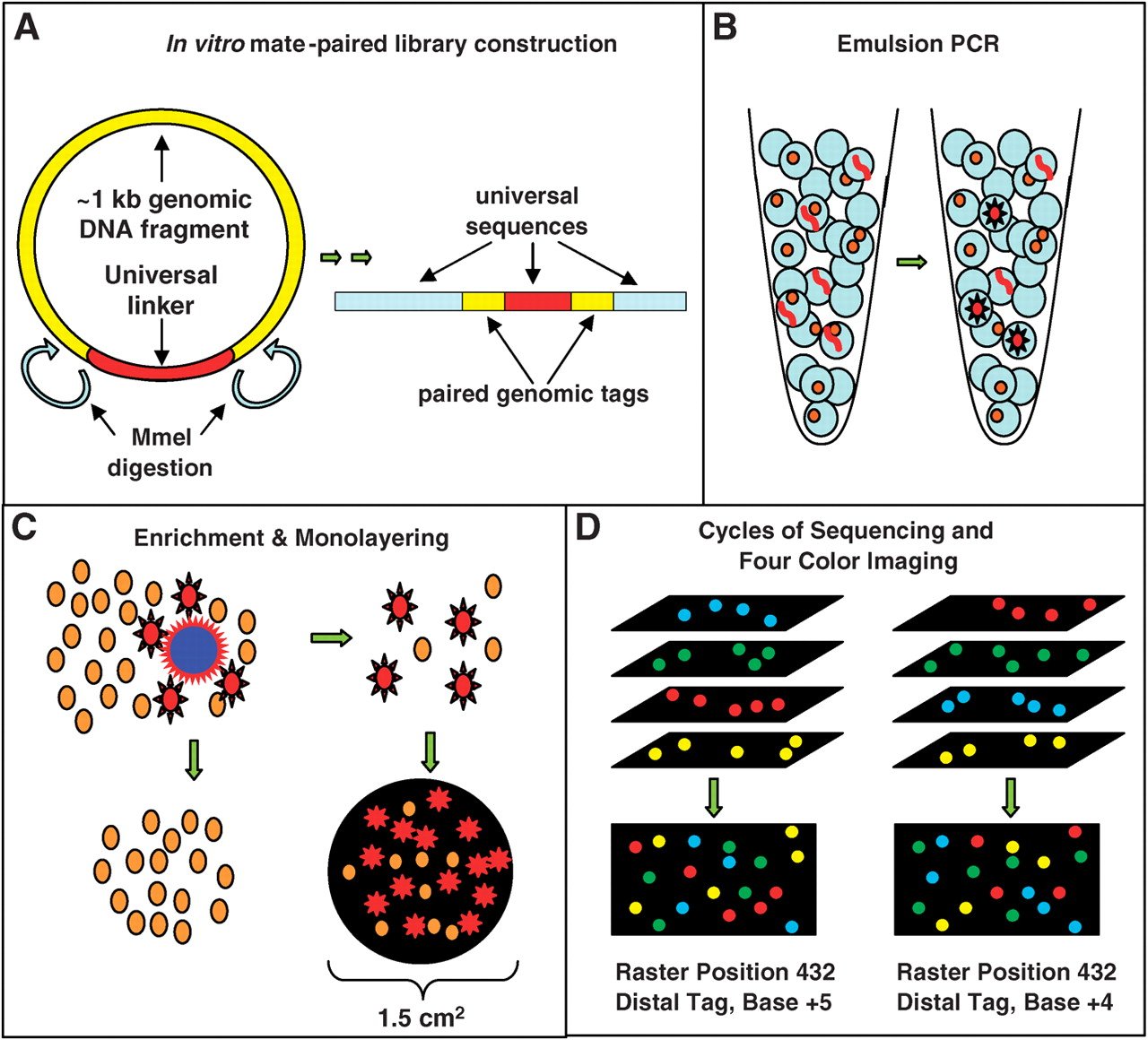
- 这是一种价格低廉但精度很高的多重测序技术,可用于同时读取数百万个固定的DNA序列。
- 这项技术最初是由哈佛医学院的乔治·丘奇博士发明的。
- 它结合了体外配对标记库、乳剂PCR、自动化显微镜和基于连接的测序化学,以> 99.9999%的准确性对大肠杆菌基因组进行测序,成本约为Sanger测序的1/10。
烟花测序
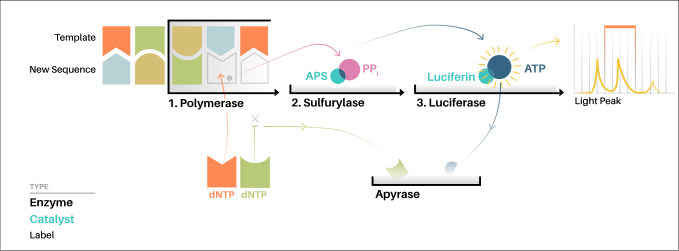
- 454生命科学公司开发了焦磷酸测序的并行版本,该公司已被罗氏诊断公司收购。
- 该方法在油溶液(乳剂PCR)中扩增水滴内的DNA,每个水滴包含一个DNA模板,连接到一个单独的引物涂层珠上,然后形成一个克隆菌落。
- 测序机包含许多皮升容积的孔,每个孔包含单个珠和测序酶。
- 焦磷酸测序使用荧光素酶产生光,用于检测添加到新生DNA的单个核苷酸,并使用组合数据生成序列读出。
- 与Sanger测序一端和Solexa和SOLiD测序另一端相比,该技术提供了中间的读取长度和每个碱基的价格。
Illumina公司(Solexa)测序
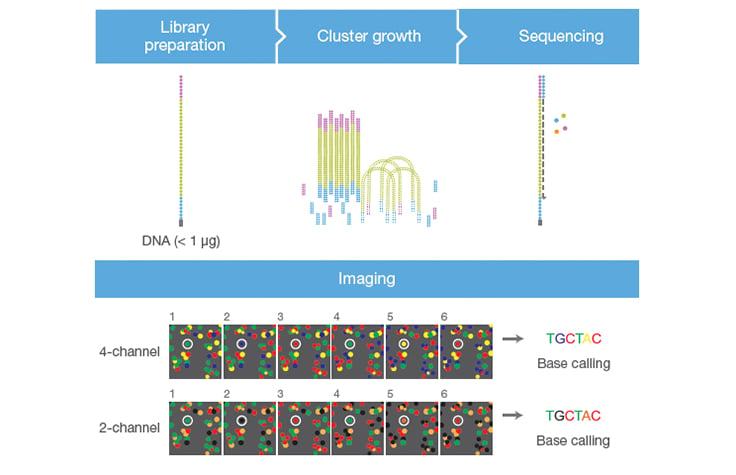
- Solexa开发了一种基于染料终止剂的测序技术。
- 在这种方法中,DNA分子首先附着在载玻片上的引物上并进行扩增。这就是所谓的桥式放大。
- 与焦磷酸测序不同的是,DNA一次只能扩增一个核苷酸。
- 摄像机拍下这些用荧光标记的核苷酸的图像,然后用化学方法将染料和末端3’阻滞剂从DNA中去除,允许下一个循环开始。
坚实的测序
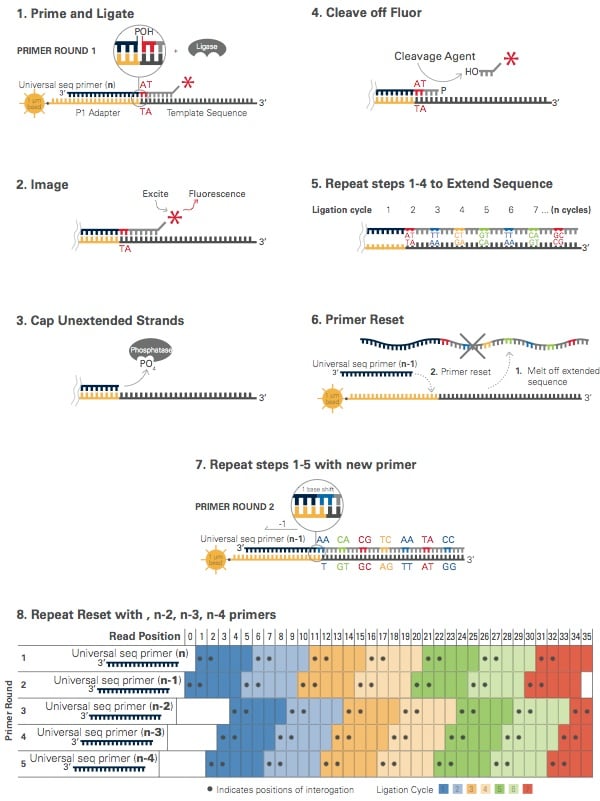
- ABISolid测序中使用的测序技术是寡核苷酸连接和检测。
- 在这个过程中,所有可能的固定长度的寡核苷酸池根据测序位置被标记。
- 这种测序结果的数量和长度序列可与illumine测序相媲美。
nanoball DNA测序
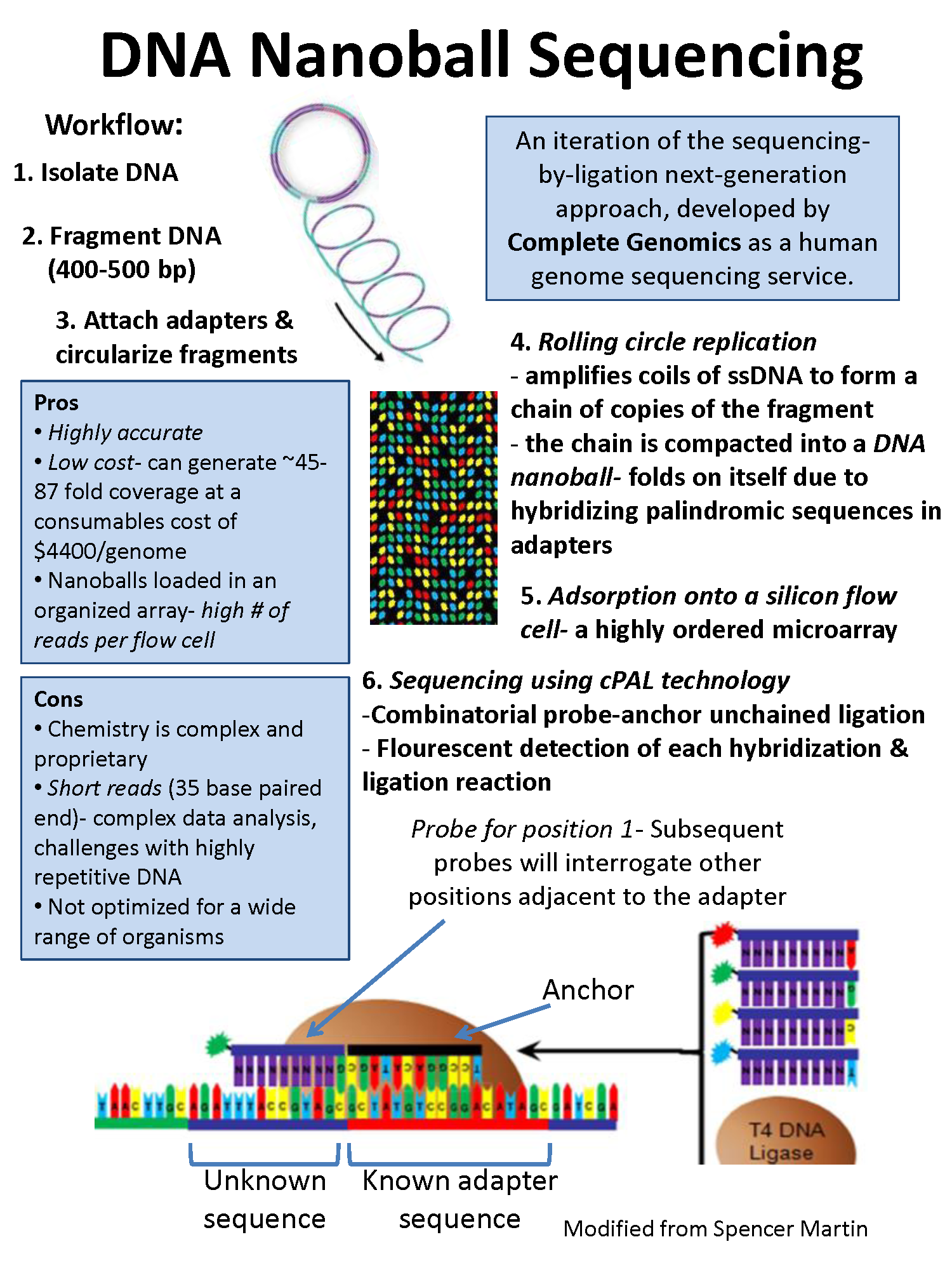
- 它是一种高通量测序技术,用于确定生物体的整个基因组序列。
- 该方法使用滚动循环复制来扩增基因组DNA分子的片段。
- 与其他下一代测序平台相比,这种DNA测序允许每次测序大量的DNA纳米球,且试剂成本较低。
- 然而,从每个DNA纳米球中只能确定DNA的短序列,这使得将短序列映射到参考基因组很困难。
- 这项技术已被用于多个基因组测序项目,并计划用于更多项目。
日光镜单分子测序
- 日光镜测序使用添加了聚a尾适配器的DNA片段,连接到流式细胞表面。
- 接下来的步骤包括扩展测序,用荧光标记的核苷酸循环洗涤流式细胞。
- 读取是由日光镜测序器执行的。
- 读取时间很短,每次运行最多55个碱基,但最近改进的方法允许更准确地读取均聚物和RNA测序。
单分子SMRT测序
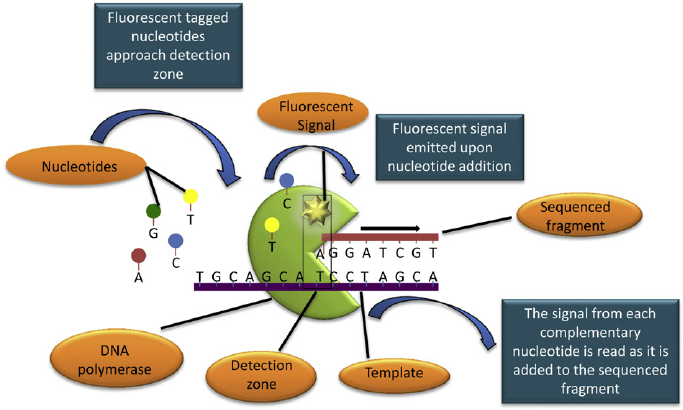
- SMRT测序基于综合测序法。
- DNA是在所谓的零模波导(ZMWs)中合成的,这是一种小的井状容器,捕获工具位于井底。
- 测序使用未修饰的聚合酶和荧光标记的核苷酸在溶液中自由流动。
- 井的构造方式是只检测到井底产生的荧光。
- 核苷酸与DNA链结合时,荧光标记与核苷酸分离,留下未修饰的DNA链。
- SMTR技术允许检测核苷酸修饰。这是通过观察聚合酶动力学发生的。
- 这种方法允许读取1000个核苷酸。
单分子实时测序(RNAP)
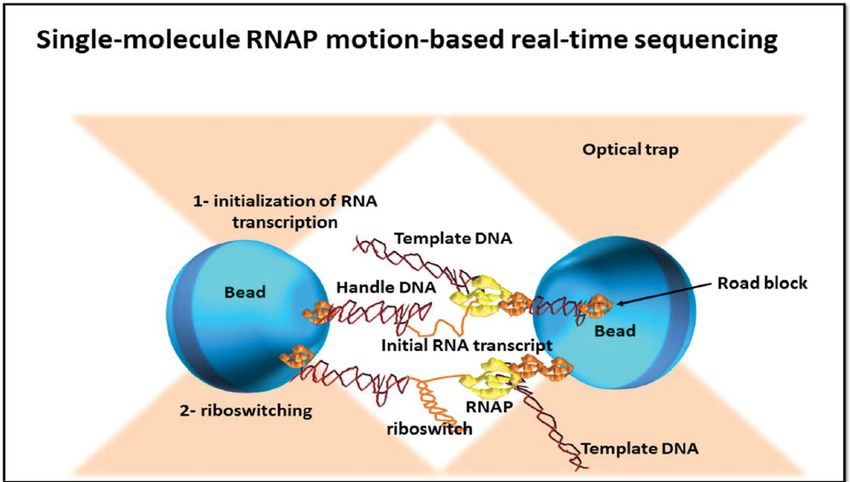
- 该方法基于RNA聚合酶(RNAP),将其连接到聚苯乙烯珠上,将测序DNA的远端连接到另一个珠上,并将两个珠置于光学阱中。
- 转录过程中的RNAP运动使小珠更近,它们的相对距离发生变化,然后可以用单核苷酸分辨率记录下来。
- 序列是根据四种核苷酸类型的浓度降低的四种读出的结果推导出来的。
参考文献
- http://library.umac.mo/ebooks/b28050393.pdf
- 大卫·海姆斯和奈杰尔·胡珀(2005)。生物化学。第三版。泰勒和弗朗西斯集团:纽约。
- 贝利,史考特,菲戈尔德,S. M.,巴伦,E. J.(1986)。贝利和斯科特的诊断微生物学。圣路易斯:处于。
- 下一代测序:优点,缺点和未来。可从:https://www.researchgate.net/publication/306431728_NextGeneration_Sequencing_Advantages_Disadvantages_and_Future[2018年9月05日访问]。
- http://www.aun.edu.eg/molecular_biology/Proceeding_Dec2011/DNA%20sequencing.pdf
- https://ab.inf.uni-tuebingen.de/teaching/ws09/bioinformatics-i/10-sequencing.pdf
- http://www.pathologyoutlines.com/topic/molecularpathdnaseqmaxam.html


仅在过去20年里,DNA测序技术就取得了长足的进步,读起来令人着迷。它可以让我们检查疾病,发现并抓住罪犯,以及研究之外的其他实际用途。感谢您解释第一代、第二代和第三代测序之间的区别。非常有趣的信息。